近日,云南大学生物交叉技术创新中心李艳团队联合多家单位在家牛基因组演化研究领域取得重要进展。研究团队通过大规模长读长测序技术,系统解析了全球家牛中由重复序列介导的结构变异的演化动态,为理解重复序列在家牛不同进化时间尺度下的变化特征提供了全新见解。该研究成果以“Deciphering the Evolution Pattern of Structural Variations Overlapped with Repetitive Sequence during Cattle Evolution”为题,于3月10日发表在国际期刊Advanced Science(影响因子14.1)上。
重复序列在动植物基因组中普遍存在,并通过非同源重组、错配修复、转座子剪切、逆转录转座等多种机制介导结构变异的产生。虽然已有大量研究表明重复序列介导的结构变异在细胞和机体层面具有重要作用,但是它们在不同进化时间尺度上如何影响和塑造基因组特征至今尚不清晰。因此研究团队选用具有各自独立进化历史和特有重复序列特征的家牛(包括瘤牛和普通牛)作为研究对象,探讨重复序列介导的结构变异(rep-SVs)在不同时间尺度下、不同进化环境中的动态变化特征。
该研究整合了覆盖全球83个家牛的长读长测序数据,构建了家牛结构变异图谱,共鉴定出209,032个非冗余结构变异,为现有的家牛结构变异数据集补充了~33.15%的新结构变异。经注释发现大约有75%的插入/缺失变异由重复序列介导的,相较于非重复序列介导的结构变异,由重复序列介导的插入/缺失变异中四个特异长度区间富集,分别是~140 bp,~280 bp,~1150 bp,~8400 bp,且不同长度的变异倾向于富集特定的重复序列。相较于常染色体,性染色体更易积累由大片段rep-SVs(>8000 bp),这种偏好积累是在长时间尺度进化过程中形成的。随后,本研究利用群落生态变化指数衡量rep-SVs在不同个体中的基因组特征,发现瘤牛(Bos indicus)在亚种分化过程中快速积累了几类重复序列类型,包括Bov-A2和LINE/Dong-R4,同时冗余分析结果显示部分重复序列频率在亚种或品种进化过程中发生特异变化,表明亚种间及品种间rep-SVs的驱动力不同。其中由Bov-A2介导的结构变异位于PDGFD基因,该基因在瘤牛的标志性瘤峰中高表达,推测可能参与亚种分化这一过程。此外,在以西门塔尔牛为代表的肉牛中鉴定到一个由卫星序列介导的62 bp缺失位于ROR2基因,该缺失通过降低与转录因子RUNX1的互作从而促进表达,斑马鱼过表达实验证明ROR2可显著促进体型增长(图1)。
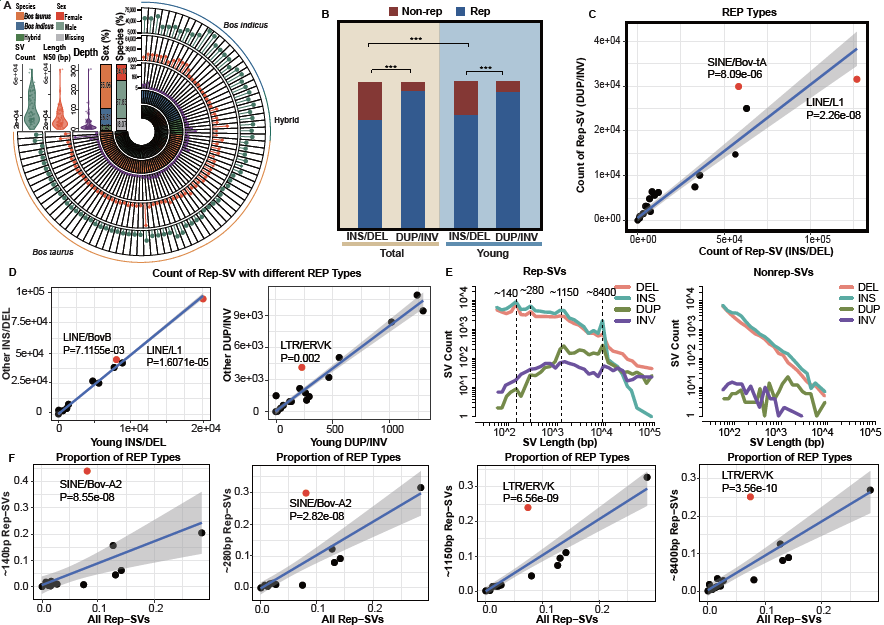
图1 家牛结构变异图谱的总体特征。A:83个家牛个体信息。B:rep-SVs和nonrep-SVs在总结构变异和年轻结构变异中的比率。C:比较介导rep-SVs的重复序列种类在不同变异类型的差异。D:rep-SVs在不同进化阶段的特征。E:rep-SVs在四个特异长度区间富集。F:重复序列种类在特异长度区间的富集情况。
本研究首次系统揭示了重复序列介导的结构变异在牛亚种分化和品种形成中的演化模式,阐明了其在基因组分布、生态群落动态及功能效应层面的复杂机制。相关成果不仅深化了对家牛基因组演化的认识,也为未来家牛种质资源创新与分子育种提供了重要的理论依据。
云南大学李艳研究员、云南大学张亚平院士、云南大学罗静教授和英国诺丁汉大学/国际家畜研究所Olivier Hanotte教授为论文的共同通讯作者。研究得到了国家重点研发计划(2021YFD1200904)、国家自然科学基金(32470654和31860305)、中央引导地方科技发展资金(202407AA110003)、云南省高校服务重点产业科技项目(FWCY-BSPY2024015)、云南省中青年学术与技术带头人基金(2018HB033)、云南省万人计划(YNWR-QNBJ-2018-124)、兴楚科技领军人才专项计划(CXKJLJRC2023-07)等项目的资助,中国科学院野生生物种质库动物分库、云南大学先进计算中心也对项目的研究提供了大力支持。
原文链接https://doi.org/10.1002/advs.202523333。
来源:生物交叉技术创新中心
编辑:张懿淼 责任编辑:李哲